
刘江研究组绘制哺乳动物着床后发育过程中DNA甲基化时空动态图谱
2026年4月27日,中国科学院生物物理研究所刘江研究组在《Nature Methods》上发表研究论文,报道了一种名为SmC-seq的空间单细胞尺度的DNA甲基化测序技术,并以此绘制了哺乳动物胚胎着床后发育过程中的DNA甲基化时空动态图谱。
如何在保留组织中细胞的空间位置信息的前提下,获得单细胞尺度的DNA甲基化图谱,在技术上难度很大。研究团队将微流控芯片系统与酶促5mC转化技术相结合,并通过原位去除组蛋白,有效降低了染色质结构对酶促反应的阻碍,从而在全基因组范围内实现了均匀的测序覆盖。该技术实现了组织切片上单细胞分辨率(10 μm)的全基因组甲基化原位检测。在通量方面,SmC-seq单次实验可同时抓取约1万个细胞。SmC-seq在保留原位空间信息的同时,其数据质量与当前的不含空间信息的单细胞甲基化技术相当。
当前,缺乏对哺乳动物胚胎着床后胚胎与母体子宫如何互作的认识,团队对该过程进行了研究。团队发现:胎盘的甲基化信息呈现双层结构,与其功能分层高度协同。尤为意外的发现是,母体子宫蜕膜细胞在胚胎着床后会发生全基因组范围的DNA去甲基化现象,这些细胞将分化为具有为哺乳动物卵黄囊形成提供营养功能的细胞。该研究首次为哺乳动物卵黄囊的形成提供了线索。
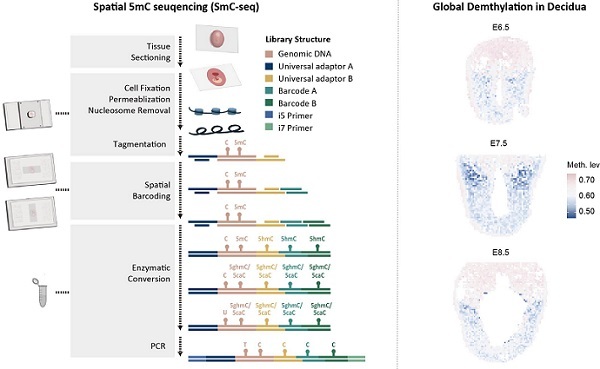
SmC-seq工作原理及其揭示的母体子宫蜕膜细胞全局去甲基化现象
左图:SmC-seq技术原理示意图。展示了SmC-seq技术的工作流程,包括组织切片、样品预处理、空间位置标定及甲基化酶学转化等关键步骤。
右图:SmC-seq应用于母体子宫蜕膜组织的检测结果。基于SmC-seq分析发现,在母体子宫蜕膜中存在部分细胞发生全局DNA去甲基化现象。
SmC-seq技术作为一种研究空间表观遗传图谱的平台,为发育、衰老及疾病等领域的相关研究开辟了新方向。中国科学院生物物理研究所的刘江研究员和高磊副研究员为论文的共同通讯作者,单循助理研究员和博士生唐益民为共同第一作者。该研究获得国家重点研发计划、中国科学院战略性先导科技专项、国家自然科学基金、深圳市医学研究基金、广东省重点领域研发计划以及广州开发区国际科技合作项目的资助。
文章链接:
https://www.nature.com/articles/s41592-026-03079-w
院英文网报道链接:
https://english.cas.cn/newsroom/research-news/202604/t20260430_1158280.shtml
(供稿:刘江研究组)
附件下载: